如何有效地操纵和组装纳米材料,一直是纳米材料应用的关键问题之一,而DNA 因其精确的碱基配对能力被广泛用于构建具有精确尺寸和明确形状的多维纳米结构。由DNA修饰的金纳米颗粒(AuNPs)具有特异性识别和精确寻址能力, 极大地扩展了金纳米颗粒在纳米组装、分析检测、药物运输、成像和基因调控中的应用。以往通常通过Au–S 键将硫化 DNA 共价偶联到AuNPs表面,而我们最近的研究发现连续腺嘌呤(polyA)能够以极高的亲和力吸附在AuNP表面;更令人惊讶的是,相较于硫化DNA,这种吸附方式能够程序可控地调整 AuNPs 表面上 DNA 分子的密度和取向。此前的研究表明,核苷酸与AuNPs表面之间的疏水相互作用在吸附中起重要作用,但polyA吸附AuNPs的机制仍然难以捉摸。2021年3月15日,浙江大学定量生物中心周如鸿教授课题组联合上海交通大学樊春海院士团队,在国际权威期刊Chemical Communications发表题为Hydrophobic Collapse-Driven Nanoparticle Coating with Poly- Adenine Adhesives的论文,提出连续腺嘌呤疏水相互作用的集体效应导致吸附过程中的疏水塌陷,对高吸附亲和力和特异性起着关键作用。

DOI: 10.1039/D1CC00628B
首先,我们研究了polyA 长度和 AuNPs 尺寸对polyA-DNA 与AuNPs结合程度的影响。实验结果表明polyA-DNA 中连续的腺嘌呤碱基倾向于完全吸附在 AuNP 表面,从而导致腺嘌呤碱基数(DNA吸附数 × polyA 长度)与吸附面积近似线性相关。我们进一步研究腺嘌呤的连续性在吸附中的作用,通过比较插入1-4 个胸腺嘧啶(T)的polyA-DNA以及腺嘌呤、胸腺嘧啶交替的DNA序列的吸附效率,我们发现:相比于腺嘌呤的总数,其连续性在polyA-DNA与AuNPs的高亲和力中起着更重要的作用。
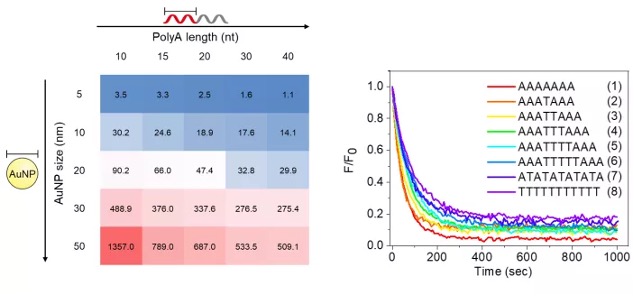
图1:实验中polyA-DNA的吸附行为
(左图:不同polyA长度和AuNP尺寸下,每个NP吸附DNA数目的热图
右图:胸腺嘧啶插入后,不同DNA序列的吸附效率图)
为了阐明上述实验现象的分子相互作用机制,我们采用经典分子动力学模拟来研究实验中polyA-DNA的吸附行为。模拟结果显示,对于胸腺嘧啶插入的polyA序列,只有连续的腺嘌呤可以吸附在AuNPs表面,而胸腺嘧啶插入区域是未结合的。此外,A3T5A3和(AT)5A之间的显著差异表明,polyA与 AuNPs 表面发生集体相互作用,导致疏水塌陷,进而引起polyA对AuNPs的强烈吸附。
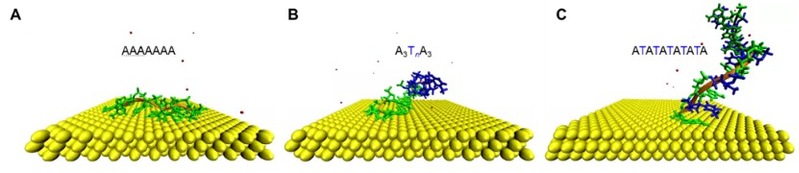
图2:经典分子动力学模拟下DNA-NP吸附图
由于polyA序列可以预测性地调节DNA-NP结构的价态、杂化热力学和动力学,这种吸附机制的发现或许能为构建更加程序可控的DNA-无机杂化纳米材料提供灵感。
本工作由南京邮电大学先进材料所,上海交通大学化学与化工学院,浙江大学定量生物中心联合完成,浙江大学周如鸿教授和上海交通大学樊春海院士为共同通讯作者。这项工作得到了国家重点研究开发项目、国家自然科学基金、国家自主创新示范区上海张江重大专项、江苏省重点研究开发项目、江苏省自然科学基金的资助。
原文链接:
https://doi.org/10.1039/D1CC00628B


